作者:小小明
10年编码经验,熟悉Java、Python和Scala,非常擅长解决各类复杂数据处理的逻辑,各类结构化与非结构化数据互转,字符串解析匹配等等。
至今已经帮助至少百名数据从业者解决工作中的实际问题,如果你在数据处理上遇到什么困难,欢迎评论区与我交流。
求每个学生分数最接近的10个学生
需求背景
某MOOC课程网站的老师需要统计每个学生成绩最相近的10个学生,距离计算公式是每门课程的成绩之差的绝对值求和。
例如,学生1的成绩为(83,84,86,99,87),学生2的成绩为(83,84,86,99,87)
两个学生的距离为|83-83|+|84-84|+|86-86|+|99-99|+|87-87|=0则判定为这两个学生成绩距离完全相同,这个距离越大说明两个学生的成绩差异越大。
下面仅使用模拟数据展示。
首先读取数据:
import pandas as pd
import numpy as np
import heapq
df = pd.read_csv("学生成绩.csv", encoding="gbk")
df.head()
结果:
这位老师管理的小班,仅100个学生。
采用双重for循环遍历每个学生与所有学生进行匹配计算,也仅1万次循环的计算量,下面我将遍历每个学生,然后内层循环再遍历每个学生进行笛卡尔积计算,最终计算出每个学生分数最接近的10个学生。
双重for循环+最小堆解决需求
data = df.values
length = data.shape[0]
names = data[:, 0]
scores = data[:, 1:]
result = []
# 遍历取出每一行的数据
for i in range(length):
# 分别取出当前遍历出来的姓名和成绩列表
name, score = names[i], scores[i]
# 用一个最小堆保存最接近的10学生
min_similar_10 = []
for j in range(length):
if i == j:
# 跳过对自己的比较
continue
# 被比较的学生姓名和成绩
find_name, find_scores = names[j], scores[j]
# 计算两个学生成绩的距离
sim_value = np.abs(score-find_scores).sum()
# 将被比较的学生和对应距离保存到最小堆中
heapq.heappush(min_similar_10, (find_name, sim_value))
# 取出10个距离最小的学生
min_similar_10 = heapq.nsmallest(10, min_similar_10, key=lambda x: x[1])
name_distance_dict = dict(min_similar_10)
name_similars, distances = list(
name_distance_dict.keys()), list(name_distance_dict.values())
result.append((name, name_similars, distances))
result = pd.DataFrame(result, columns=["姓名", "分数最接近的10个学生", "距离"])
result
最终结果:

仅耗时120毫秒以内,说明双重for循环的算法在100数据量时,可以顺利解决这个问题的。
下面简单介绍一下最小堆:
堆是数据结构中最常见的一种数据结构,是一个完全二叉树。最小堆中每一个节点的值都小于等于其子树中每个节点的值。
具体的原理,学过数据结构的读者都懂,没有学过的也不用深究。
上面的代码中使用最小堆的目的是为了避免排序,采用堆化方式查找N个最小值,基于最小堆的查找,时间复杂度在O(logN)~O(N)之间,
远比排序的时间复杂度O(nlogN)快。
关于heapq的官方文档:https://docs.python.org/zh-cn/3/library/heapq.html?highlight=heapq#module-heapq
heapq的实现源码:https://github.com/python/cpython/blob/3.9/Lib/heapq.py
如果你对堆的实现原理感兴趣,可以参考数据结构学习笔记:
https://datastructure.xiaoxiaoming.xyz/#/16.%E5%A0%86
好景不长,该MOOC网站的管理员后面又希望把历史班级所有学生的分数最接近的10个学生都找出来,大概有1W以上的学生。用上面的代码跑了一下,10分钟左右也跑出了结果,感觉我的代码处理效果还不错。
我自己也测试了一下1万条测试数据:
df = pd.read_csv("学生成绩_10000.csv", encoding="gbk")
data = df.values
length = data.shape[0]
names = data[:, 0]
scores = data[:, 1:]
result = []
# 遍历取出每一行的数据
for i in range(length):
# 分别取出当前遍历出来的姓名和成绩列表
name, score = names[i], scores[i]
# 用一个最小堆保存最接近的10学生
min_similar_10 = []
for j in range(length):
if i == j:
# 跳过对自己的比较
continue
# 被比较的学生姓名和成绩
find_name, find_scores = names[j], scores[j]
# 计算两个学生成绩的距离
sim_value = np.abs(score-find_scores).sum()
# 将被比较的学生和对应距离保存到最小堆中
heapq.heappush(min_similar_10, (find_name, sim_value))
# 取出10个距离最小的学生
min_similar_10 = heapq.nsmallest(10, min_similar_10, key=lambda x: x[1])
name_distance_dict = dict(min_similar_10)
name_similars, distances = list(
name_distance_dict.keys()), list(name_distance_dict.values())
result.append((name, name_similars, distances))
result = pd.DataFrame(result, columns=["姓名", "分数最接近的10个学生", "距离"])
result
结果:
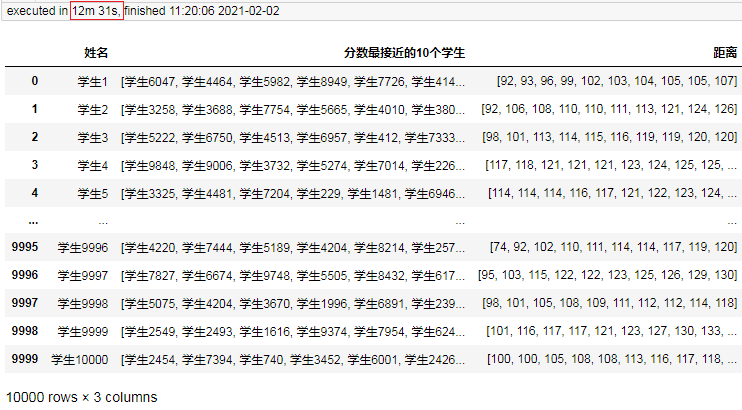
耗时是12.5分钟。
虽然网站管理员对这个代码已经满意,但对于我来说速度还是太慢,要跑这么大的数据量,代码还是优化一下比较好,于是我使用numpy向量化操作,使程序在2分钟内对1万条数据跑出了结果。下面是处理代码:
使用numpy向量化操作解决需求
考虑到部分读者没有看懂最小堆的操作,这次我将分步拆解下面这套代码的处理逻辑。
首先对本文开头的100条数据进行测试,获取源数据的姓名和分数数组:
import pandas as pd
import numpy as np
import heapq
df = pd.read_csv("学生成绩.csv", encoding="gbk")
data = df.values
length = data.shape[0]
names = data[:, 0]
scores = data[:, 1:]
print(names[:5])
print(scores[:5])
结果:
['学生1' '学生2' '学生3' '学生4' '学生5']
[[71 82 81 84 73 95 62 96 96 87 61 78 79 89 98 80]
[57 91 99 74 93 93 58 74 89 84 63 62 78 57 94 74]
[72 59 76 60 99 71 73 74 72 74 85 79 100 88 80 91]
[71 62 81 80 57 84 92 95 63 59 84 64 90 58 60 75]
[83 62 95 76 57 75 97 57 65 63 84 73 74 59 62 93]]
遍历第一次就break结束,取出第一个学生用于测试:
for i in range(length):
name, score = names[i], scores[i]
print(name, score)
break
结果:
学生1 [77 89 60 99 83 80 95 93 94 82 92 93 96 98 70 84]
利用numpy广播变量的特性一次性求出该学生与所有学生(含自己)的距离:
score_diff = np.abs(scores-score).sum(axis=1)
score_diff
结果:
array([0, 322, 248, 203, 215, 366, 198, 224, 299, 229, 274, 240, 253, 238,
183, 239, 223, 344, 320, 221, 291, 264, 273, 309, 307, 243, 258,
231, 225, 185, 234, 324, 315, 247, 247, 232, 179, 210, 238, 261,
175, 252, 259, 254, 330, 270, 193, 248, 252, 214, 175, 219, 262,
256, 265, 249, 263, 180, 270, 294, 260, 195, 272, 240, 213, 181,
252, 292, 261, 233, 238, 205, 237, 241, 244, 234, 255, 151, 228,
241, 173, 174, 221, 248, 191, 249, 243, 224, 252, 266, 229, 231,
228, 346, 232, 273, 269, 336, 294, 277], dtype=object)
由于上面的距离包含自身,所以先取出距离最短的11个学生的索引,再删除自身的索引:
min_similar_index = np.argpartition(score_diff, 11)[:11].tolist()
min_similar_index.remove(i)
min_similar_index
结果:
[77, 80, 81, 40, 50, 36, 57, 65, 14, 29]
根据这10个学生的索引读取所需要的数据:
name_similars = names[min_similar_index]
distances = score_diff[min_similar_index]
print(name_similars)
print(distances)
结果:
['学生78' '学生81' '学生82' '学生41' '学生51' '学生37' '学生58' '学生66' '学生15' '学生30']
[151 173 174 175 175 179 180 181 183 185]
这样我们就已经计算出该学生成绩最接近的10个学生的姓名和距离。
然后整理一下完整处理代码:
import pandas as pd
import numpy as np
import heapq
df = pd.read_csv("学生成绩.csv", encoding="gbk")
data = df.values
length = data.shape[0]
names = data[:, 0]
scores = data[:, 1:]
result = []
for i in range(length):
name, score = names[i], scores[i]
score_diff = np.abs(scores-score).sum(axis=1)
min_similar_index = np.argpartition(score_diff, 11)[:11].tolist()
min_similar_index.remove(i)
name_similars = names[min_similar_index]
distances = score_diff[min_similar_index]
result.append((name, name_similars, distances))
result = pd.DataFrame(result, columns=["姓名", "分数最接近的10个学生", "距离"])
result
结果:

下面再针对一万条数据跑一跑:
df = pd.read_csv("学生成绩_10000.csv", encoding="gbk")
data = df.values
length = data.shape[0]
names = data[:, 0]
scores = data[:, 1:]
result = []
for i in range(length):
name, score = names[i], scores[i]
score_diff = np.abs(scores-score).sum(axis=1)
min_similar_index = np.argpartition(score_diff, 11)[:11].tolist()
min_similar_index.remove(i)
name_similars = names[min_similar_index]
distances = score_diff[min_similar_index]
result.append((name, name_similars, distances))
result = pd.DataFrame(result, columns=["姓名", "分数最接近的10个学生", "距离"])
result
结果:
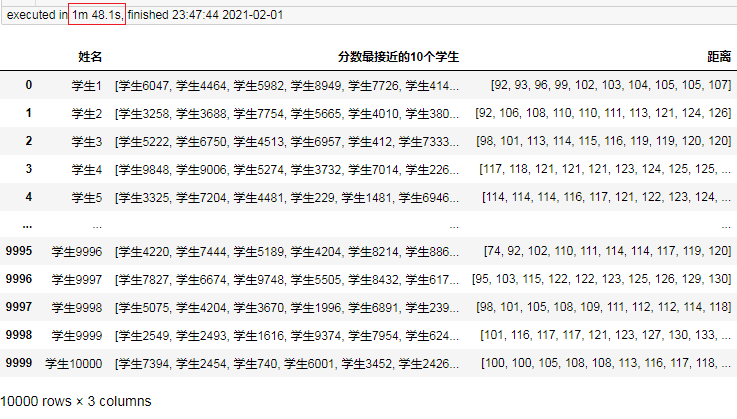
可以看到耗时为1分48秒,相对直接使用笛卡尔积快了很多倍。
使用ball_tree解决需求
虽然上面的优化已经大幅度提升了程序性能,但毕竟仍然需要双重遍历O(n^2)时间复杂度的方法。万一哪天网站要求对10万个学生进行计算呢?时间又要多翻了几十倍,耗时要达到好几个小时。我转而一想直接用KNN内部的ball_tree来解决这个问题吧。
(关于使用KNN查找最近点的问题可参考很早之前的一篇文章:https://blog.csdn.net/as604049322/article/details/112385553)
先使用10000条学生成绩的数据进行测试,读取这10000条学生成绩数据:
df = pd.read_csv("学生成绩_10000.csv", encoding="gbk")
df
结果:
然后取出需要被训练的数据:
# 取出用于被KNN训练的数据
data = df.iloc[:, 1:].values
# y本身用于标注每条数据属于哪个类别,但我们并不使用KNN的分类功能,所以统一全部标注为类别0
y = np.zeros(data.shape[0], dtype='int8')
print(data[:5])
print(y[:5])
结果:
[[ 77 89 60 99 83 80 95 93 94 82 92 93 96 98 70 84]
[ 90 63 72 57 100 85 63 62 67 77 82 68 81 79 100 71]
[ 71 71 82 72 62 70 82 63 92 69 97 97 82 69 63 57]
[ 88 78 88 61 72 61 77 93 94 88 86 95 84 70 73 94]
[ 66 67 59 70 75 67 79 74 57 84 96 67 93 87 58 83]]
[0 0 0 0 0]
创建KNN训练器,并进行训练:
from sklearn.neighbors import KNeighborsClassifier
knn = KNeighborsClassifier(n_neighbors=1, algorithm='ball_tree', p=1)
knn.fit(data, y)
distance, similar_points = knn.kneighbors(
data, n_neighbors=11, return_distance=True)
distance = distance.astype("int", copy=False)
print(distance[:5])
print(similar_points[:5])
结果:
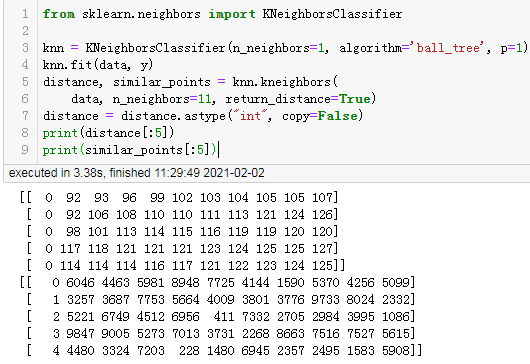
训练耗时为3.4秒。
n_neighbors是KNN用来分类的参数,我们并不使用分类,将其指定的越小,越能减少无用的计算量,但是这个参数必须比0大,所以我指定为1。
而需求方要求的距离计算公式显然就等价于曼哈顿距离,所以我将p指定为1。
knn.kneighbors则用来计算最近的点,n_neighbors指定为11是因为结果会包含自身,后面去除自身后结果是10。
由于sklearn最终计算出来的距离是float浮点数类型,而这个需求只可能产生整数距离,所以将其转换为整数。
上面训练完就相当于已经计算出了结果,下面我再将结果整理成需要的格式:
names = df['姓名']
result = []
for i, name in names.iteritems():
name_similar_indexs = similar_points[i].tolist()
self_index = name_similar_indexs.index(i)
name_similar_indexs.pop(self_index)
name_similars = names[name_similar_indexs].tolist()
distances = distance[i].tolist()
distances.pop(self_index)
result.append((name, name_similars, distances))
result = pd.DataFrame(result, columns=["姓名", "分数最接近的10个学生", "距离"])
result
结果:
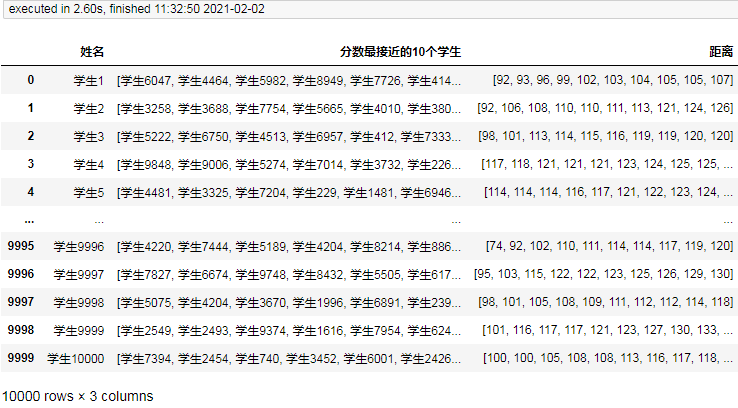
对于10000条数据ball_tree的计算总耗时为5秒左右。可见相对于前面的双重遍历的方法速度已经提高了N倍。
关于KD-tree算法和Ball-tree算法的原理可参考:
https://www.cnblogs.com/eyeszjwang/articles/2429382.html
https://www.cnblogs.com/lesleysbw/p/6074662.html
https://www.zhihu.com/question/30957691
对4万条学生模拟数据进行测试
为了测试方便,不再用excel来生成数据,而是直接使用python。
python直接生成测试数据的方法,以生成10条数据为例:
size = 100000
data = np.c_[np.arange(1, size+1).reshape((-1, 1)),
np.random.randint(56, 101, size=(size, 16))]
df = pd.DataFrame(data, columns=["姓名", "Python", "C/C++", "Java", "Scala", "数据结构", "离散数学",
"计算机体系结构", "编译原理", "计算机网络", "数据库原理", "计算机图形学",
"自然语言处理", "嵌入式系统及应用", "网络信息与安全", "计算机视觉", "人工智能"])
df["姓名"] = "学生"+df["姓名"].astype(str)
df
结果:
然后使用上面相同的代码分别测试1w条、2w条、3w条、…、10w条:

1万条耗时5.3秒。
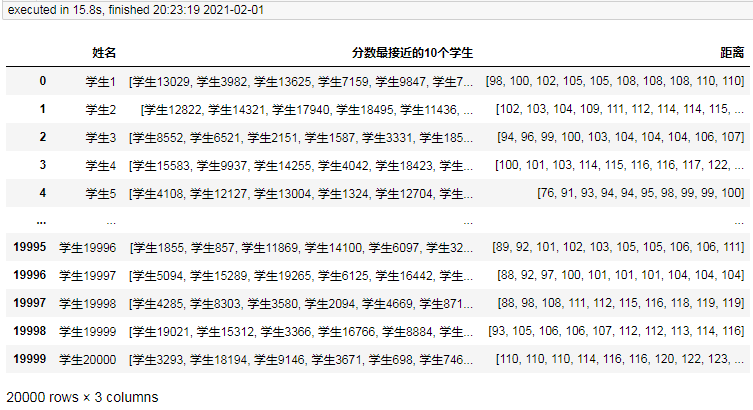
2万条耗时15.8秒。
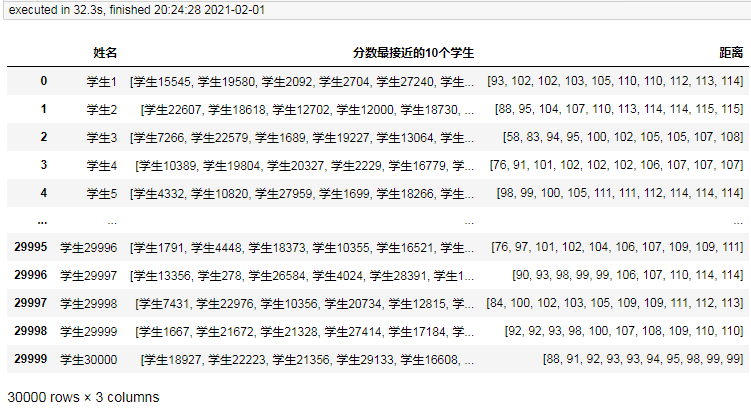
3万条耗时32.3秒。
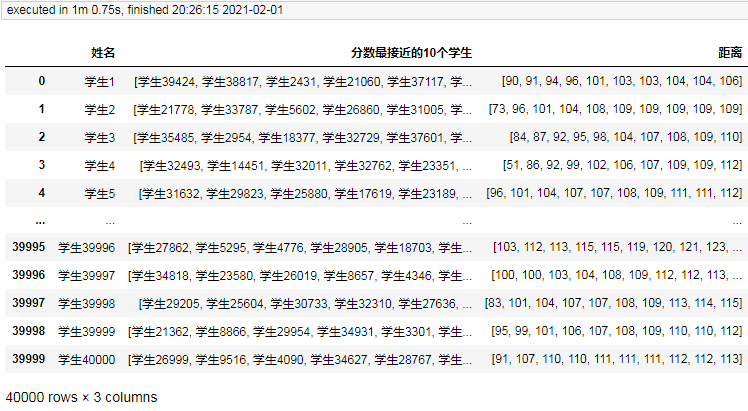
4万条耗时60.75秒。
预估10万条数据的耗时
这时间增长趋势好像也不是线性增长而是指数增长,下面先就记录一下多少条记录时耗时多久吧:
import pandas as pd
import numpy as np
import time
from sklearn.neighbors import KNeighborsClassifier
times = {
}
for size in np.r_[np.arange(1000, 10001, 1000), np.arange(20000, 60001, 10000)]:
data = np.c_[np.arange(1, size+1).reshape((-1, 1)),
np.random.randint(56, 101, size=(size, 16))]
df = pd.DataFrame(data, columns=["姓名", "Python", "C/C++", "Java", "Scala", "数据结构", "离散数学",
"计算机体系结构", "编译原理", "计算机网络", "数据库原理", "计算机图形学",
"自然语言处理", "嵌入式系统及应用", "网络信息与安全", "计算机视觉", "人工智能"])
df["姓名"] = "学生"+df["姓名"].astype(str)
start_time = time.perf_counter()
# 取出用于被KNN训练的数据
data = df.iloc[:, 1:].values
# y本身用于标注每条数据属于哪个类别,但我并不使用KNN的分类功能,所以统一全部标注为类别0
y = np.zeros(data.shape[0], dtype='int8')
knn = KNeighborsClassifier(n_neighbors=1, algorithm='ball_tree', p=1)
knn.fit(data, y)
distance, similar_points = knn.kneighbors(
data, n_neighbors=11, return_distance=True)
distance = distance.astype("int", copy=False)
names = df['姓名']
result = []
for i, name in names.iteritems():
name_similar_indexs = similar_points[i].tolist()
self_index = name_similar_indexs.index(i)
name_similar_indexs.pop(self_index)
name_similars = names[name_similar_indexs].tolist()
distances = distance[i].tolist()
distances.pop(self_index)
result.append((name, name_similars, distances))
result = pd.DataFrame(result, columns=["姓名", "分数最接近的10个学生", "距离"])
take_time = time.perf_counter()-start_time
print(f"{size}条数据耗时{take_time:.2f}秒")
times[size] = take_time
time_df = pd.DataFrame.from_dict(times, orient='index', columns=["time"])
结果:
1000条数据耗时0.29秒
2000条数据耗时0.59秒
3000条数据耗时0.98秒
4000条数据耗时1.40秒
5000条数据耗时1.97秒
6000条数据耗时2.44秒
7000条数据耗时3.00秒
8000条数据耗时3.74秒
9000条数据耗时4.41秒
10000条数据耗时5.23秒
20000条数据耗时15.92秒
30000条数据耗时31.75秒
40000条数据耗时64.25秒
50000条数据耗时132.26秒
60000条数据耗时220.87秒
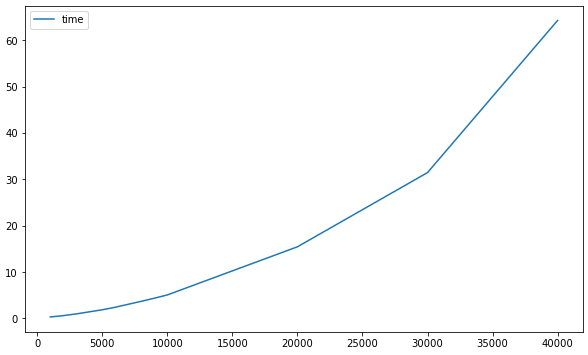
从这走势来看有点像二次函数或幂次函数,我们假设这是一个二次函数然后使用numpy拟合这条曲线,并预估10万数据的耗时:
from numpy import polyfit, poly1d
import matplotlib.pyplot as plt
%matplotlib inline
x = np.arange(1000, 100001, 1000)
y = poly1d(polyfit(time_df.index, time_df.time, 2))
plt.figure(figsize=(10, 6))
plt.plot(time_df.index, time_df.time, 'rx')
plt.plot(x, y(x), 'b:')
plt.show()
print(f"10万条数据预计耗时{y(100000):.2f}秒")
结果:
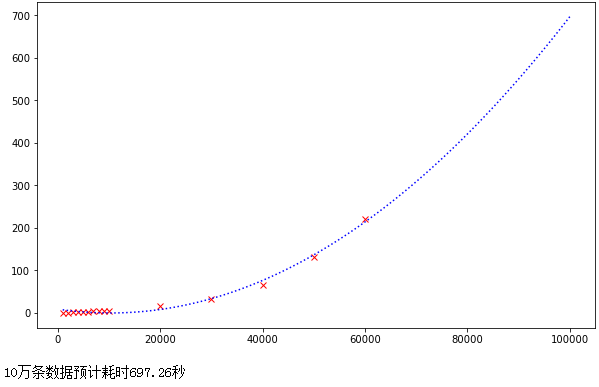
预计耗时11分钟。
不过实际测试了一下,12分钟也并没有出结果,说明曲线拟合的效果还不是太准。
认真观察原始数据(红色点)和拟合曲线(蓝色线),可能这个曲线实际并不是二次函数,而是三次以上的函数或幂次函数,下面使用3次函数进行拟合:
from numpy import polyfit, poly1d
import matplotlib.pyplot as plt
%matplotlib inline
x = np.arange(1000, 100001, 1000)
y = poly1d(polyfit(time_df.index, time_df.time, 3))
plt.figure(figsize=(10, 6))
plt.plot(time_df.index, time_df.time, 'rx')
plt.plot(x, y(x), 'b:')
plt.show()
print(f"10万条数据预计耗时{y(100000):.2f}秒")
结果:
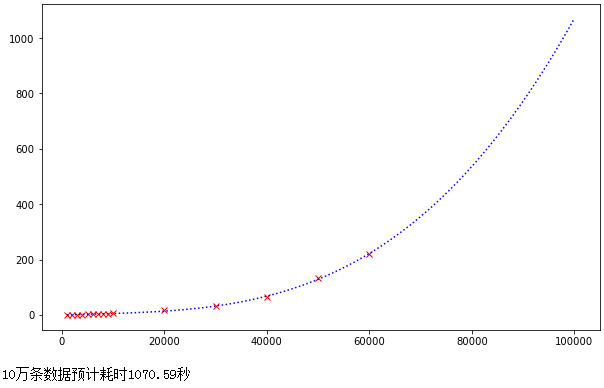
预估耗时为17分钟。
实际耗时呢?
import pandas as pd
import numpy as np
from sklearn.neighbors import KNeighborsClassifier
size = 100000
data = np.c_[np.arange(1, size+1).reshape((-1, 1)),
np.random.randint(56, 101, size=(size, 16))]
df = pd.DataFrame(data, columns=["姓名", "Python", "C/C++", "Java", "Scala", "数据结构", "离散数学",
"计算机体系结构", "编译原理", "计算机网络", "数据库原理", "计算机图形学",
"自然语言处理", "嵌入式系统及应用", "网络信息与安全", "计算机视觉", "人工智能"])
df["姓名"] = "学生"+df["姓名"].astype(str)
# 取出用于被KNN训练的数据
data = df.iloc[:, 1:].values
# y本身用于标注每条数据属于哪个类别,但我并不使用KNN的分类功能,所以统一全部标注为类别0
y = np.zeros(data.shape[0], dtype='int8')
knn = KNeighborsClassifier(n_neighbors=1, algorithm='ball_tree', p=1)
knn.fit(data, y)
distance, similar_points = knn.kneighbors(
data, n_neighbors=11, return_distance=True)
distance = distance.astype("int", copy=False)
names = df['姓名']
结果:
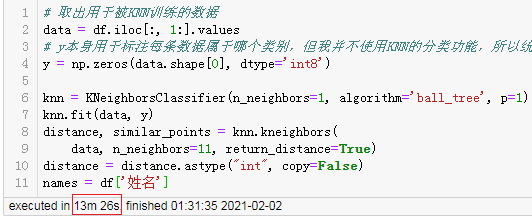
训练耗时13分钟。
from tqdm.notebook import tqdm
result = []
pbar = tqdm(total=size)
for i, name in names.items():
pbar.update(1)
name_similar_indexs = similar_points[i].tolist()
self_index = name_similar_indexs.index(i)
name_similar_indexs.pop(self_index)
name_similars = names[name_similar_indexs].tolist()
distances = distance[i].tolist()
distances.pop(self_index)
result.append((name, name_similars, distances))
pbar.close()
result = pd.DataFrame(result, columns=["姓名", "分数最接近的10个学生", "距离"])
result
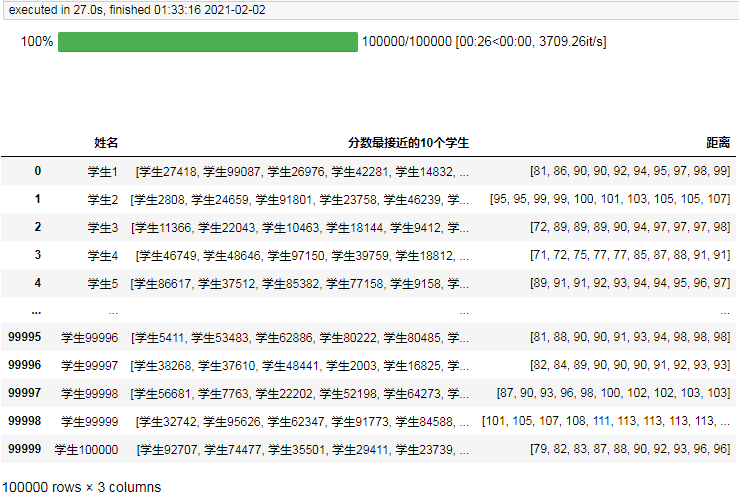
整理结果耗时半分钟,实际耗时是14分钟。
虽然14分钟也比较慢,但相对前面的笛卡尔积的算法需要耗时好几小时而言已经大幅度提升程序计算性能,节约了计算时间。
总结
今天我向你演示了如何使用最小堆和numpy来快速计算每个学生分数最接近的10个学生,可以看到在数据量小于一万时,这种笛卡尔积的算法还可以接受,但一旦达到2万以上,基本上就慢的难以忍受了。所以我使用ball_tree来计算这个距离,1W数据量仅耗时5秒。
但是当数据量达到5万以上时,ball_tree也有点慢了,但也相对笛卡尔积的算法还是快了很多。
最后,我使用numpy拟合时间曲线,在二次函数的拟合下预估10w数据量时ball_tree的耗时为12分钟,三次函数的拟合下是17分钟。而实际测试的结果是14分钟,介于2者之间。
欢迎下方留言或评论,分享你的看法。